Streszczenia publikacji
Tutaj będę dzielić się krótkimi, nieformalnymi omówieniami najnowszych artykułów (a może także niektórych starszych).
Filament formation and NAD processing by noncanonical human FAM118 sirtuins
Baretić, D.✱, Missoury, S.✱, Patel, K., Martinez, M., Coste, F., Zhu, K., Smith, R., Kopasz, A. G., Yang, L., Bigot, N., Chapuis, C., Riou, R., Đukić, N., Goffinont, S., Pressoir, V., Patačko, S., Timinszky, G., Delarue, M., Castaing, B., Ahel, D., Mikoč, A., Huet, S.✉, Ahel, I.✉ & Suskiewicz, M.J.✉
Filament formation and NAD processing by noncanonical human FAM11_B sirtuins. Nature Structural & Molecular Biology 32 (2025).
Link do artykułu
W niedawnym badaniu prowadzonym we współpracy zbadaliśmy białka FAM118 – niekanoniczne sirtuiny, które tworzą filamenty i przetwarzają NAD w komórkach ludzkich i innych kręgowców. Siedem kanonicznych ludzkich sirtuin, SIRT1-SIRT7, to dobrze poznane enzymy związane z aktywnością deacetylacji białek. Jednak ludzie posiadają dwa dodatkowe, słabo scharakteryzowane białka o fałdzie sirtuinowym, FAM118B i FAM118A. W tej pracy zbadaliśmy ich ewolucję, strukturę i funkcję molekularną.
W skrócie pokazujemy, że ludzkie FAM118 są bliższe ancestralnym bakteryjnym sirtuinom niż kanonicznym ludzkim SIRTom; że tworzą filamenty in vitro i w komórkach; że mają aktywność przetwarzania NAD (prawdopodobnie hydrolizy NAD); oraz że mieszanie dwóch paralogów, FAM118B i FAM118A, wzmacnia aktywność.
Była to ścisła współpraca z laboratorium Ivana Ahela (Dunn School, Oxford), laboratorium Sébastiena Hueta (IGDR Rennes) i innymi zespołami. Wszyscy autorzy byli ważni, ale chciałbym wyróżnić Domagoja Bareticia i Sophię Missoury (z Franckiem Coste) za ich eksperymenty cryoEM i inne testy, oraz Sébastiena Hueta i jego zespół za doskonałe eksperymenty optyczne. Wyróżniam także Andreję za jej analizę filogenetyczną, Karishmę za eksperymenty dotyczące przetwarzania NAD, a przede wszystkim Ivana za jego intuicję, energię i hojność.
Białka FAM118 od dawna interesowały Ivana (mojego kierownika postdoka), który, jak w wielu innych przypadkach, miał dobrą intuicję co do ich znaczenia. Były jednak trudnym celem biochemicznym. Nasz zespół – z naszym zainteresowaniem samoorganizacją białek – wniósł obserwację, że homooligomeryzują się w filamenty, co zbadaliśmy wspólnie w ramach tego projektu.
Chciałbym również zwrócić uwagę na niedawną publikację Bernheima, Poiriera i współpracowników w Science, pokazującą, że FAM118B, które nazywają „SIRal”, jest niezbędne dla wrodzonej odpowiedzi immunologicznej w komórkowych modelach ssaków; mają również świetną analizę filogenetyczną i wgląd w biochemię.
Dziękuję naszym wspaniałym laboratoriom (CBM UPR4301, Dunn School, IGDR Rennes i Instytut Pasteura) oraz źródłom finansowania, w tym Agence Nationale de la Recherche, ERC i Wellcome Trust. Dziękuję również Nature Structural & Molecular Biology za bardzo konstruktywny proces recenzji.
RING dimerisation drives higher-order organisation of SINA/SIAH E3 ubiquitin ligases
Coste, F.✉, Mishra, A., Chapuis, C., Mance, L., Pukało, Z., Bigot, N., Goffinont, S., Gaudon, V., Garnier, N., Talhaoui, I., Castaing, B., Huet, S.✉, Suskiewicz, M.J.✉
RING dimerisation drives higher-order organisation of SINA/SIAH E3 ubiquitin ligases. The FEBS Journal, 5/2/2025.
Link do artykułu. Jeśli powyższy link nie zapewnia wolnego dostępu, wersja autorska jest dostępna tutaj
Z przyjemnością dzielimy się naszym nowym badaniem pokazującym, że ligaza E3 ubikwityny SIAH1, o której wiadomo, że dimeryzuje poprzez swój C-terminalny SBD, dimeryzuje również poprzez swój N-terminalny RING. Kiedy te tendencje łączą się w pełnej długości białku, SIAH1 tworzy multimery, co może wyjaśniać jego lokalizację w klastrach w komórkach i preferencję dla zagregowanych/multimerycznych substratów.
Projekt zaczął się, gdy Zosia była studentką na stażu letnim i dyskutowaliśmy o świetnym artykule Słabickiego i in. Ubikwitylacja BCL6 przez SIAH1 jest wzmacniana, gdy BCL6 zostaje zmultimeryzowany przez małą cząsteczkę. Dlaczego SIAH1 preferencyjnie celuje w multimeryczną wersję białka? Doszliśmy do wniosku, że SIAH1 może być również multimerem i rozpoznawać multimery poprzez awidność.
Skrystalizowaliśmy i Franck rozwiązał strukturę krystalograficzną dimeru utworzonego przez część RING-ZnF1 SIAH1. Potwierdziliśmy dimeryzację w roztworze metodą SEC-RALS/LALS i zwalidowaliśmy mutację V90R jako blokującą dimeryzację RING. Aanchal wykonała piękne modelowanie AlphaFold pokazujące dimeryzację w całej rodzinie SINA/SIAH. Warto dodać, że rodzina SINA/SIAH jest obecna w wielu gatunkach, od roślin po ludzi, i jest wysoce konserwowana. To, co mówimy o SIAH1 w tym artykule, najprawdopodobniej dotyczy wszystkich członków rodziny, a wykonujemy również eksperymenty z SINA drosophili i ludzkim SIAH2.
Oto co dzieje się w komórkach: SIAH1 znakowany mCherry (co prawda nieco nadeksprymowany) lokalizuje się w wydłużonych klastrach, ale potrzebne są do tego zarówno RING, jak i SBD, i brak mutacji V90R – w przeciwnym razie SIAH1 jest w większości rozproszony. Gdy patrzymy na kolokalizację ze zagregowanym substratem, Synphilin-1, SIAH1 WT kolokalizuje, ale jest to w dużej mierze uniemożliwione, gdy blokujemy dimeryzację domeny RING mutacją V90R. Prowadzi to nas do modelu, w którym multimeryzacja umożliwia wiązanie substratów wielowartościowych o wysokiej awidności.
Na koniec, Lucija wykonała piękne eksperymenty ubikwitylacji in vitro pokazujące, że mutant V90R fragmentu RING-ZnF1 jest upośledzony w tworzeniu długich łańcuchów ubikwityny. Istnieje zatem również rola dimeryzacji RING w katalizowaniu poliubikwitylacji, jak obserwowano dla innych dimerycznych ligaz E3 z RING.
Ogólnie ten poboczny projekt jest związany z naszym ciągłym zainteresowaniem tym, jak multimeryzacja substratów i ligaz – w szczególności tworzenie filamentów – wpływa na procesy SUMOylacji i ubikwitylacji. Dziękuję wszystkim kolegom i współpracownikom zaangażowanym w ten projekt i Tobie za uwagę ;).
Oto projekt okładki, który nie został zaakceptowany, pokazujący multimery SIAH1 nad komórkami (SIAH1 na czerwono, aktyna na zielono). Warto zauważyć, że nie byliśmy w stanie zobrazować łańcuchów SIAH1 in vitro, ponieważ mogliśmy oczyścić jedynie N- lub C-terminalne połówki SIAH1 oddzielnie: niebieskie łańcuchy to modele zbudowane z połączonych dimerycznych struktur każdej połówki.
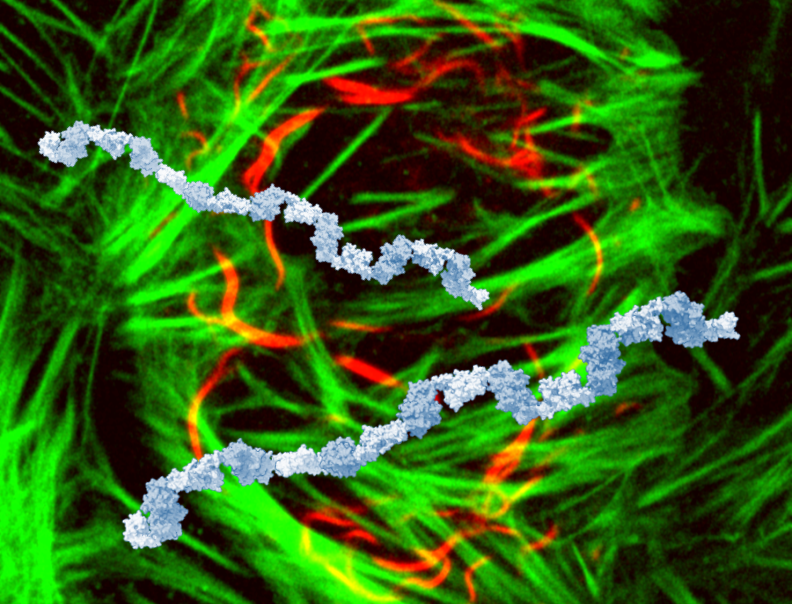
Ostatecznie trafiliśmy na okładkę FEBS Journal, ale z innym obrazem.
Dynamic BTB-domain filaments promote clustering of ZBTB proteins
Mance, L., Bigot, N., Sánchez, E. Z., Coste, F.✉, Martín-González, N., Zentout, S., Biliškov, M., Pukało, Z., Mishra, A., Chapuis, C., Arteni, A.-A., Lateur, A., Goffinont, S., Gaudon, V., Talhaoui, I., Casuso, I., Beaufour, M., Garnier, N., Artzner, F., Cadene, M., Huet, S., Castaing, B., Suskiewicz, M. J.✉.
Dynamic BTB-domain filaments promote clustering of ZBTB proteins. Molecular Cell, 84(13), 2490-2510. (2024).
Link do artykułu. Jeśli powyższy link nie działa, wersja autorska jest dostępna tutaj
W tym artykule pokazujemy, że domeny BTB białek ZBTB, w tym ZBTB8A i ZBTB18, tworzą homomultimery, co koncentruje je w ogniskach jądrowych i przyczynia się do ich funkcji jako represorów. Demonstrujemy i charakteryzujemy tę właściwość za pomocą krystalografii, różnych metod biofizycznych i biologii komórkowej. Filamenty BTB są zbudowane z dimerów połączonych głowa-do-głowy, sklejonych ogon-do-ogona. Różnią się topologią od filamentów głowa-do-ogona tworzonych przez znane domeny polimeryzujące takie jak SAM. Te różnice mają implikacje dla ewolucji i przewidywania filamentów, jak dyskutujemy w naszym artykule.
Zainteresowaliśmy się białkami ZBTB, ponieważ pracujemy nad PTM zwaną SUMOylacją, a białka te należą do najsilniej SUMOylowanych. Uważaliśmy, że domeny BTB mogą oddziaływać z enzymem E2 SUMO, UBC9. Dlaczego? Dla przynajmniej jednego białka ZBTB (ZBTB1) wykazano, że SUMOylacja tego białka zależy od obecności domeny BTB, mimo że domena BTB jest fizycznie oddalona od miejsca SUMOylacji. Ponadto w SLX4, któremu przypisywano aktywność ligazy E3 SUMO, znajduje się domena BTB, o której wykazano, że przyczynia się do tej proponowanej aktywności. W połączeniu z faktem, że białka ZBTB są bardzo silnie SUMOylowane i kilka z nich, zgodnie z doniesieniami, oddziałuje z UBC9 (ZBTB8A, ZBTB9, ZBTB7A, ZBTB26, ZBTB2, ZBTB16, ZBTB1), wyglądało na to, że domena BTB może być domeną oddziałującą z UBC9. Zaczęliśmy od domeny BTB ZBTB8A, która została umiarkowanie przekonująco zamodelowana jako oddziałująca z UBC9 przez AlphaFold2. Niestety, pomimo tych różnorodnych wskazówek, nie znaleźliśmy wyraźnych dowodów eksperymentalnych na to, że domeny BTB białek ZBTB oddziałują z UBC9. Zamiast tego okazało się, że tworzą filamenty, co szczegółowo zbadaliśmy w tej pracy. Uważamy, że filamentacja może pośrednio sprzyjać SUMOylacji (pracujemy nad tym).
Między innymi fakt, że znaleźliśmy skłonność do filamentacji w rodzinie białek uważanej za stosunkowo dobrze scharakteryzowaną, sugeruje, że białek tworzących filamenty jest więcej, niż obecnie sądzimy. Jednym z powodów, by tak uważać, jest to, że białka tworzące filamenty są często nierozpuszczalne przy rekombinowanej nadekspresji, a zatem trudne do badania. To ekscytujące czasy dla tej dziedziny, ponieważ AlphaFold może czasem przewidzieć tę tendencję, ułatwiając poszukiwanie nowych białek tworzących filamenty. Tendencja do tworzenia filamentów może wyjaśniać niektóre przypadki formowania ognisk w komórkach – alternatywne, a może uzupełniające wyjaśnienie wobec separacji fazowej.
Wielką frajdą było dokonanie tego przypadkowego odkrycia i zbudowanie wokół niego projektu. Zaczęło się jako projekt magisterski, a teraz doktorski, Luciji Mance, doskonałej doktorantki. Wielkie podziękowania dla Francka, Sébastiena, Martine i wszystkich innych wspaniałych współautorów i współpracowników z Orleanu, Rennes, Paryża/Gif-sur-Yvette, Marsylii. I bardzo nas cieszy, że mogliśmy skoordynować jednoczesną publikację z grupami Paula Parka, Jiho Parka, Fischera i Eberta z Dana-Farber/Harvard. Ich artykuł został właśnie opublikowany.
DELTEX E3 ligases ubiquitylate ADP-ribosyl modification on nucleic acids
Kang, Z. ✉, Suskiewicz, M.J., Chatrin, C., Strømland, Ø., Dorsey, B. W., Aucagne, V., Ahel, D. ✉, Ahel, I. ✉
Nucleic Acids Research, 24 November 2023, gkad1119
Link do artykułu w otwartym dostępie
To jest kontynuacja badania opublikowanego rok wcześniej i dostępnego tutaj. Oba były prowadzone głównie przez Kanga i Ivana, z wkładem innych autorów w tym moim, szczególnie w poprzednim artykule. Bardzo się też ucieszyłem, że stało się to współpracą z innym naukowcem z CBM w Orleanie, naszym wspaniałym przyjacielem-chemikiem, Vincentem Aucagne’em.
Dla tych z Państwa, którzy nie są zaznajomieni z ADP-rybozylacją, powinienem może zacząć od tego, że NAD+ nie jest tylko centralną cząsteczką energetyczną w komórce, ale może być też wykorzystywany do szczególnego typu modyfikacji białek zwanej ADP-rybozylacją, katalizowanej przez rodzinę enzymów zwanych PARPami. Podczas ADP-rybozylacji mała część NAD+ zwana nikotynamidem odłącza się, a reszta NAD+ (część ADP-rybozy) przyłącza się kowalencyjnie do białka przez atom węgla, do którego był przyłączony nikotynamid.
Kilka PARPów wydaje się być pseudoenzymami, które są w rzeczywistości nieaktywne. Jednym z nich jest PARP9, który tworzy konstytutywny kompleks z ligazą E3 ubikwityny DTX3L. Powiedziałem, że PARP9 wydaje się nieaktywny, ale gdy jest razem z DTX3L i gdy obecne są składniki kaskady ubikwitynowej (enzym E1, enzym E2, ATP), obserwuje się solidną reakcję między NAD+ a ubikwityną, jak wykazała grupa Paschala sześć lat temu.
W obecności tych składników (PARP9, DTX3L, E1, E2 i ATP), NAD+ (lub jego część) w jakiś sposób łączy się z ubikwityną. Czym jest ta reakcja? Zaproponowano, że jest to ADP-rybozylacja ubikwityny: nikotynamid prawdopodobnie odłącza się od NAD+, część ADP-rybozy NAD+ przyłącza się do ubikwityny przez atom węgla na ADP-rybozie, do którego był przyłączony nikotynamid. Tak jak w każdym innym wydarzeniu ADP-rybozylacji białka katalizowanym przez PARPy.
Powinienem dodać, że kilka lat później grupa Huanga – a w szczególności Chatrin Chatrin, który od tego czasu dołączył do grupy Ivana i jest współautorem artykułu Kanga w NAR – wykazała, że w rzeczywistości PARP9 jest zbędny dla tej reakcji. Potrzebne jest białko DTX – albo DTX3L, albo jeden z jego ludzkich homologów z rodziny DTX – a także E1, E2 i ATP. Minimalnym fragmentem DTX3L, który jest potrzebny, jest domena RING i przylegająca domena wiążąca NAD+/ADP-rybozę zwana DTC.
Co wniosły dwa artykuły Kanga do tej historii? Wykazały – moim zdaniem przekonująco – że ta tajemnicza reakcja in vitro między NAD+ a ubikwityną, którą katalizują białka DTX, nie jest kanoniczną ADP-rybozylacją. Nikotynamid się nie odłącza, NAD+ pozostaje nienaruszony, a ubikwityna wiąże się kowalencyjnie przez wiązanie estrowe z jedną z grup hydroksylowych rybozy NAD+. Vincent Aucagne (z pomocą Hervé Meudala z naszej platformy NMR) odegrał kluczową rolę w identyfikacji miejsca przyłączenia Ub.
Nie przemieszcza się nikotynamidu podczas reakcji i w rzeczywistości nikotynamid w ogóle nie musi być obecny. Tak więc reakcja DTX działa również z ADP-rybozą. W rzeczywistości ADP-ryboza jest preferowana nad NAD+ jako substrat. I – co najciekawsze – enzymy DTX mogą ubikwitylować ADP-rybozę przyłączoną do białka lub peptydu w wyniku wcześniejszej reakcji ADP-rybozylacji.
To jest nowa chemia, i potencjalnie bardzo fascynująca, ponieważ ubikwityluje się białko nie na reszcie lizyny, co byłoby typowe, ale na potranslacyjnej modyfikacji ADP-rybozy. W rezultacie otrzymuje się podwójną modyfikację ubikwityna-ADP-ryboza, która mogłaby mieć swoją odrębną funkcję w komórce?
I teraz kolejny zwrot akcji. Okazuje się, że DTX3L posiada domeny wiążące kwasy nukleinowe. Ostatnio wykazano, że niektóre PARPy mogą ADP-rybozylować nie tylko białka, ale także kwasy nukleinowe (czy to rzeczywiście zachodzi w komórce, nie jest jeszcze jasne). Czy więc DTX3L mógłby ubikwitylować ADP-rybozę przyłączoną do kwasów nukleinowych? Okazuje się, że tak, i robi to bardziej solidnie, jeśli użyte jest pełnej długości białko z domenami wiążącymi kwasy nukleinowe.
Ważny punkt: te badania opisują dość solidne i specyficzne reakcje in vitro, ale pozostają do zademonstrowania w komórce.
I ostatni punkt. Jestem świadomy, że w schematach w obu artykułach jest błąd we wzorze ADP-rybozy: jedna ryboza ma złą stereochemię. Błąd pochodzi ode mnie i jest zawstydzający, biorąc pod uwagę, że pracuję nad ADP-rybozą od kilku lat. Jestem wdzięczny chemikowi obecnemu na sali, gdy dawałem wykład ubiegłego lata, który zwrócił mi uwagę na coś, co zawsze przeoczyłem. Przepraszam Kanga i innych kolegów, którzy ufając mi, skopiowali lub przeoczyli ten błąd. Mam nadzieję, że nie odwróci to uwagi czytelnika od eleganckich eksperymentów Kanga i ich fascynujących wniosków.
ADP-ribosylation from molecular mechanisms to therapeutic implications
Suskiewicz, M. J., Prokhorova, E., Rack, J.G.M., Ahel, I.✉
Cell, 2023, Oct 12;186(21):4475-95.
Link do artykułu w otwartym dostępie
Nowy obszerny artykuł przeglądowy na temat ADP-rybozylacji, napisany wspólnie z byłymi kolegami z grupy Ivana Ahela w Dunn School w Oxfordzie (jestem bardzo wdzięczny Ivanowi za tę możliwość oraz Evgenii i Johannesowi za wspólną pracę).
ADP-rybozylacja jest fundamentalną reakcją modyfikacji biochemicznej, w której ADP-ryboza jest przenoszona z NAD+ na substrat (typowo białko). Wiele rund ADP-rybozylacji może skutkować tworzeniem łańcuchów poli(ADP-rybozy). Modyfikacja ADP-rybozą może regulować różne aspekty funkcji biomolekularnych, w szczególności oddziaływania. Ponieważ istnieje kilka domen i motywów białkowych rozpoznających ADP-rybozylację, modyfikacja ta może indukować nowe oddziaływania białko:białko. Inhibitory głównego ludzkiego enzymu ADP-rybozylacji, PARP1, są z powodzeniem stosowane w klinice do celowania w określone typy nowotworów. W tym przeglądzie, pisanym przez kilka ostatnich miesięcy, staraliśmy się objąć szeroki zakres, obejmując chemię, biologię strukturalną, mechanizmy enzymatyczne, różnorodne szlaki komórkowe i wreszcie zastosowania kliniczne.
Jestem zadowolony z tego przeglądu, z wyjątkiem znaku ładunku dodatniego (plus), który został przypadkowo umieszczony na etapie produkcji na odłączonym nikotynamidzie na pierwszej figurze.
Structural insights into the regulation of the human E2∼SUMO conjugate through analysis of its stable mimetic
Goffinont, S., Coste, F., Prieu-Serandon, P., Mance, L., Gaudon, V., Garnier, N., Castaing, B., Suskiewicz, M. J. ✉
Journal of Biological Chemistry, 2023, 299(7)
Link do artykułu w otwartym dostępie
Podczas ubikwitylacji i pokrewnych reakcji ubikwityna lub pokrewny modyfikator jest najpierw ładowany na resztę Cys w enzymie E2, tworząc tioester E2-modyfikator. Modyfikator jest następnie przenoszony stamtąd na resztę Lys w substracie białkowym, często z pomocą ligazy E3.
SUMOylacja jest zasadniczą modyfikacją typu ubikwityny. Podczas gdy ubikwitylacja opiera się na licznych enzymach E2, SUMOylacja zależy od jednego jedynego, UBC9, który jest zatem centralnym białkiem szlaku. UBC9 jest wysoce konserwowane – jego sekwencja niewiele się zmienia od drożdży do ludzi.
Ponieważ tioestery E2-modyfikator są niestabilne, naszym celem było wyprodukowanie stabilnego mimetyku ludzkiego UBC9-SUMO. Zastosowaliśmy strategię opracowaną przez znakomitą grupę Limy dla drożdżowego Ubc9, polegającą na wprowadzeniu reszty Lys blisko w przestrzeni do Cys93 miejsca aktywnego UBC9. Opisujemy naszą realizację tej strategii w szczegółach i pokazujemy, że SUMO efektywnie migruje z Cys93 na Lys umieszczoną w pozycji 129 dzięki mutacji Ala129Lys, tworząc stabilną cząsteczkę z SUMO przyłączonym 3 Å od swojej natywnej pozycji w tioestrze UBC9-SUMO.
Skrystalizowaliśmy ten mimetyk. W nieobecności ligazy E3 przyjmuje on tak zwaną konformację otwartą, która odpowiadałaby prawdopodobnie nieaktywnemu stanowi tioestru. Rzeczywiście, wszystkie wcześniejsze struktury UBC9-SUMO były z ligazą E3, która stabilizowała stan zamknięty. Co ciekawe, w krysztale mimetyk tworzy łańcuchy poprzez niekowalencyjne oddziaływanie między SUMO z jednej cząsteczki UBC9-SUMO a UBC9 z następnej. Uważamy, że takie oddziaływania mogą się czasem tworzyć w komórkach, sterrycznie zniechęcając aktywny, zamknięty stan UBC9-SUMO. Inny interesujący punkt dotyczy Cys138 – eksponowanej na powierzchni Cys w UBC9 o niejasnej funkcji. W naszej strukturze krystalicznej w konformacji otwartej Cys138 jest blisko Cys52 SUMO i pozornie zostały one połączone krzyżowo przez DTT. Czy te reszty Cys mogłyby tworzyć mostek disiarczkowy w pewnych warunkach w komórkach?
Są też inne elementy tej historii. Położyliśmy nacisk na szczegółowy opis i dyskusję. Bylibyśmy zadowoleni, gdyby okazało się to użyteczne dla naszej dziedziny.
To jest część szerszej linii badawczej, w której próbujemy różnych biochemicznych i chemicznych sposobów stabilizacji kompleksów SUMOylacji. To pierwsza publikacja z naszego projektu SUMOwriteNread. Nasz inżynier Stéphane Goffinont grał pierwsze skrzypce (dzięki i gratulacje!), z pomocą Francka Coste (struktura krystaliczna), Pierre’a Prieu-Serandona i reszty zespołu.
Mamy krótki popularny opis artykułu po angielsku na stronie naszego Centrum.
Updated protein domain annotation of the PARP protein family sheds new light on biological function
Suskiewicz, M. J. ✉✱, Munnur, D.✱, Strømland, Ø.✱, Yang, J. C., Easton, L. E., Chatrin, C., Zhu, K., Baretić, D., Goffinont, S., Schuller, M., Wu, W.-F., Elkins, J. M., Ahel, A., Sanyal, S., Neuhaus, D., Ahel, I. ✉
Nucleic Acids Research, 2023, 51(15):8217-8236
Link do artykułu w otwartym dostępie
W tym artykule, będącym efektem projektu pobocznego, starannie przeanalizowaliśmy modele AlphaFold2 ludzkich członków rodziny białek PARP, dokonaliśmy kompleksowej anotacji domen, uzyskaliśmy nowe wglądy w strukturę i funkcję, i eksperymentalnie zwalidowaliśmy niektóre z nich.
Mamy nadzieję, że anotacja domen będzie użytecznym zasobem. Uważamy, że wszystkie strukturalne domeny w PARPach są teraz oznaczone. Niektóre nie były wcześniej opisane – na przykład domeny KH, które są potencjalnymi domenami wiążącymi RNA lub jednoniciowy DNA ze specyficznością sekwencyjną, w PARP9, 10 i 14.
Ja wykonałem większość analizy obliczeniowej i pisania, podczas gdy Deeksha i Øyvind z laboratorium Ivana Ahela (mojej byłej grupy) przeprowadzili eksperymenty wykazujące, że fragmenty PARP14 mogą rzeczywiście wiązać się z kwasami nukleinowymi i ADP-rybozylować je in vitro. Zespół Davida Neuhausa z MRC LMB w Cambridge wniósł interesujący eksperyment NMR pokazujący, że podczas gdy poszczególne domeny PARP1 mają niezależną mobilność w stanie wolnym od DNA, większość z nich skupia się razem po związaniu z przerwą w DNA – z wyjątkiem domeny BRCT, która pozostaje elastyczna.
We wstępie staraliśmy się w prosty sposób wyjaśnić zasady stojące za AlphaFold2 i przedstawić różne niedawne, łatwe w użyciu narzędzia do analizy białek. Mamy nadzieję, że ta część może zainteresować nawet osoby pracujące nad innymi rodzinami białek.
Instytut Chemii CNRS poświęcił temu artykułowi ładny artykuł popularnonaukowy po francusku, a na stronie naszego Centrum mamy też krótką notkę po angielsku.