Résumés de publications
Ici, je partage de courtes discussions informelles sur les articles les plus récents (et peut-être aussi quelques articles plus anciens).
Filament formation and NAD processing by noncanonical human FAM118 sirtuins
Baretić, D.✱, Missoury, S.✱, Patel, K., Martinez, M., Coste, F., Zhu, K., Smith, R., Kopasz, A. G., Yang, L., Bigot, N., Chapuis, C., Riou, R., Đukić, N., Goffinont, S., Pressoir, V., Patačko, S., Timinszky, G., Delarue, M., Castaing, B., Ahel, D., Mikoč, A., Huet, S.✉, Ahel, I.✉ & Suskiewicz, M.J.✉
Filament formation and NAD processing by noncanonical human FAM11_B sirtuins. Nature Structural & Molecular Biology 32 (2025).
Lien vers l’article
Dans cette étude collaborative récente, nous avons étudié les protéines FAM118, des sirtuines non canoniques qui forment des filaments et traitent le NAD dans les cellules humaines et d’autres vertébrés. Les sept sirtuines humaines canoniques, SIRT1-SIRT7, sont des enzymes bien étudiées associées à l’activité de déacétylation des protéines. Cependant, les humains possèdent deux autres protéines à domaine sirtuine moins bien caractérisées, FAM118B et FAM118A. Dans ce travail, nous avons étudié leur évolution, leur structure et leur fonction moléculaire.
En bref, nous montrons que les FAM118 humaines sont plus proches des sirtuines bactériennes ancestrales que des SIRTs humaines canoniques ; qu’elles s’assemblent en filaments in vitro et dans les cellules ; qu’elles ont une activité de traitement du NAD (vraisemblablement d’hydrolyse du NAD) ; et que le mélange des deux paralogues, FAM118B et FAM118A, stimule l’activité.
Ce travail est le fruit d’une collaboration étroite avec le laboratoire d’Ivan Ahel (Dunn School, Oxford), le laboratoire de Sébastien Huet (IGDR Rennes), et d’autres équipes. Tous les auteurs ont joué un rôle important, mais je tiens à souligner les contributions de Domagoj Baretić et Sophia Missoury (avec Franck Coste) pour leurs expériences de cryoEM et autres, et de Sébastien Huet et son équipe pour leurs excellentes expériences d’optique. Je mets également en avant Andreja pour son analyse phylogénétique, Karishma pour les expériences de traitement du NAD, et surtout Ivan pour son intuition, son énergie et sa générosité.
Les FAM118 intéressaient Ivan (mon directeur de post-doc) depuis longtemps ; comme dans bien d’autres cas, il avait eu une bonne intuition quant à leur importance. Cependant, elles se sont révélées être une cible biochimique difficile. Notre équipe – avec notre intérêt pour l’auto-assemblage des protéines – a apporté l’observation qu’elles s’homo-oligomérisent en filaments, une découverte explorée de manière collaborative dans cette étude.
Je tiens également à souligner une publication récente de Bernheim, Poirier et collègues dans Science, montrant que FAM118B, qu’ils nomment « SIRal », est essentielle à la réponse immunitaire innée dans des modèles cellulaires de mammifères ; ils présentent également une excellente analyse phylogénétique et des perspectives biochimiques.
Je remercie nos excellents laboratoires (CBM UPR4301, la Dunn School, l’IGDR Rennes et l’Institut Pasteur) ainsi que les sources de financement, notamment l’Agence Nationale de la Recherche, l’ERC et le Wellcome Trust. Je remercie également Nature Structural & Molecular Biology pour un processus de révision très constructif.
RING dimerisation drives higher-order organisation of SINA/SIAH E3 ubiquitin ligases
Coste, F.✉, Mishra, A., Chapuis, C., Mance, L., Pukało, Z., Bigot, N., Goffinont, S., Gaudon, V., Garnier, N., Talhaoui, I., Castaing, B., Huet, S.✉, Suskiewicz, M.J.✉
RING dimerisation drives higher-order organisation of SINA/SIAH E3 ubiquitin ligases. The FEBS Journal, 5/2/2025.
Lien vers l’article. Si le lien précédent ne fonctionne pas pour accéder en libre accès, vous pouvez consulter la version auteurs ici
Nous sommes heureux de partager notre nouvelle étude montrant que la ligase E3 d’ubiquitine SIAH1, connue pour dimériser via son SBD C-terminal, dimérise également via son RING N-terminal. Lorsque ces deux tendances se combinent dans la protéine entière, SIAH1 forme des multimères, ce qui pourrait expliquer sa localisation en clusters dans les cellules et sa préférence pour les substrats agrégés/multimériques.
Le projet a commencé quand Zosia était étudiante stagiaire et que nous discutions de l’excellent article de Słabicki et al. L’ubiquitylation de BCL6 par SIAH1 est renforcée lorsque BCL6 est multimérisé par une petite molécule. Pourquoi SIAH1 cible-t-il préférentiellement la version multimérique d’une protéine ? Nous avons raisonné que SIAH1 pourrait être aussi un multimère et reconnaître les multimères par avidité.
Nous avons cristallisé et Franck a résolu la structure cristallographique du dimère formé par la partie RING-ZnF1 de SIAH1. Nous avons confirmé la dimérisation en solution par SEC-RALS/LALS et validé la mutation V90R comme bloquant la dimérisation par le RING. Aanchal a réalisé de très belles modélisations avec AlphaFold montrant la dimérisation à travers la famille SINA/SIAH. Il faut ajouter que la famille SINA/SIAH est présente dans de nombreuses espèces, des plantes aux humains, et est hautement conservée. Ce que nous décrivons pour SIAH1 dans cet article s’applique très probablement à tous les membres de la famille, et nous effectuons d’ailleurs quelques expériences avec SINA de drosophile et SIAH2 humaine.
Voici ce qui se passe dans les cellules : SIAH1 marqué mCherry (certes, un peu surexprimé) se localise en clusters allongés, mais il faut que RING et SBD soient présents, et que la mutation V90R soit absente, sinon SIAH1 est principalement diffus. Quand on examine la colocalisation avec un substrat agrégé, Synphilin-1, SIAH1 WT colocalise, mais cela est largement empêché lorsqu’on bloque la dimérisation du domaine RING avec la mutation V90R. Cela nous conduit à un modèle où la multimérisation permet une liaison de haute avidité aux substrats multivalents.
Enfin, Lucija a réalisé de belles expériences d’ubiquitylation in vitro montrant que le mutant V90R du fragment RING-ZnF1 est déficient dans la production de longues chaînes d’ubiquitine. Il y a donc aussi un rôle de la dimérisation du RING dans la catalyse de la polyubiquitylation, comme observé pour d’autres ligases E3 à RING dimériques.
Dans l’ensemble, ce projet annexe est lié à notre intérêt continu pour la façon dont la multimérisation des substrats et des ligases – en particulier la formation de filaments – affecte les processus de SUMOylation et d’ubiquitylation. Je remercie tous les collègues et collaborateurs impliqués dans ce projet et vous pour votre attention ;).
Voici un projet de couverture qui n’a pas été retenu, montrant les multimères de SIAH1 au-dessus des cellules (SIAH1 en rouge, actine en vert). À noter que nous n’avons pas pu visualiser les chaînes de SIAH1 in vitro, car nous n’avons pu purifier que les moitiés N- ou C-terminales de SIAH1 séparément : les chaînes bleues sont des modèles construits à partir des structures dimériques combinées de chaque moitié.
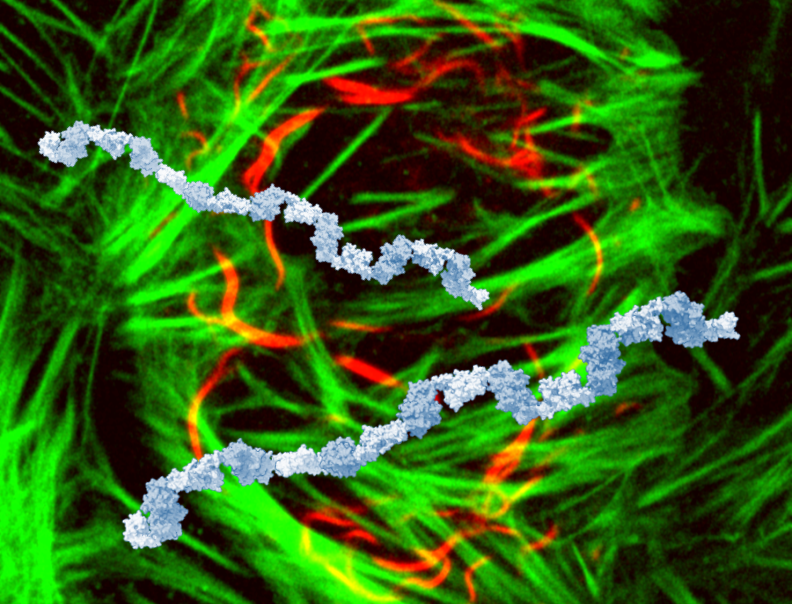
En fait, nous avons fini par apparaître en couverture du FEBS Journal, mais avec une image différente.
Dynamic BTB-domain filaments promote clustering of ZBTB proteins
Mance, L., Bigot, N., Sánchez, E. Z., Coste, F.✉, Martín-González, N., Zentout, S., Biliškov, M., Pukało, Z., Mishra, A., Chapuis, C., Arteni, A.-A., Lateur, A., Goffinont, S., Gaudon, V., Talhaoui, I., Casuso, I., Beaufour, M., Garnier, N., Artzner, F., Cadene, M., Huet, S., Castaing, B., Suskiewicz, M. J.✉.
Dynamic BTB-domain filaments promote clustering of ZBTB proteins. Molecular Cell, 84(13), 2490-2510. (2024).
Lien vers l’article. Si le lien précédent ne fonctionne pas, vous pouvez accéder à la version auteurs ici
Dans cet article, nous montrons que les domaines BTB des protéines ZBTB, y compris ZBTB8A et ZBTB18, forment des homomultimères, ce qui les concentre dans des foyers nucléaires et contribue à leur fonction de répresseurs. Nous démontrons et caractérisons cette propriété par cristallographie, diverses méthodes biophysiques et de la biologie cellulaire. Les filaments BTB sont constitués de dimères tête-à-tête connectés queue-à-queue. Ils diffèrent en topologie des filaments tête-à-queue formés par les domaines polymérisants connus comme SAM. Ces différences ont des implications pour l’évolution et la prédiction des filaments, comme discuté dans notre article.
Nous nous sommes intéressés aux ZBTBs parce que nous travaillons sur une PTM appelée SUMOylation, et ces protéines sont parmi les plus fortement SUMOylées. Nous pensions que les domaines BTB pourraient interagir avec l’enzyme E2 SUMO, UBC9. Pourquoi ? Pour au moins une protéine ZBTB (ZBTB1), il a été montré que la SUMOylation de cette protéine dépend de la présence du domaine BTB, bien que le domaine BTB soit physiquement éloigné du site de SUMOylation. De plus, dans SLX4, qui aurait une activité ligase E3 SUMO, il y a un domaine BTB qui a été montré comme contribuant à cette activité proposée. Combiné au fait que les protéines ZBTB sont très fortement SUMOylées et que plusieurs d’entre elles ont été rapportées comme interagissant avec UBC9 (ZBTB8A, ZBTB9, ZBTB7A, ZBTB26, ZBTB2, ZBTB16, ZBTB1), il semblait que le domaine BTB pourrait être un domaine interagissant avec UBC9. Nous avons commencé avec le domaine BTB de ZBTB8A, modélisé de manière modérément convaincante comme interagissant avec UBC9 par AlphaFold2. Hélas, malgré ces indices, nous n’avons pas trouvé de preuve expérimentale claire que les domaines BTB des ZBTBs interagissent avec UBC9. En revanche, il s’est avéré qu’ils forment des filaments, que nous avons étudiés en détail dans cette étude. Nous pensons que la filamentation pourrait indirectement favoriser la SUMOylation (nous travaillons actuellement dessus).
Entre autres, le fait d’avoir trouvé une propension à la filamentation dans une famille de protéines considérée comme relativement bien caractérisée suggère qu’il y a plus de protéines formant des filaments que ce que nous pensons actuellement. L’une des raisons de le penser est que les protéines formant des filaments sont fréquemment insolubles lors de la surexpression recombinante et donc difficiles à étudier. C’est une période passionnante pour ce domaine, car AlphaFold peut parfois prédire cette tendance, facilitant ainsi la recherche de nouvelles protéines formant des filaments. La tendance à former des filaments pourrait expliquer certains cas de formation de foyers dans les cellules – une explication alternative, ou peut-être complémentaire, à la séparation de phase.
C’était très agréable de faire cette découverte fortuite et de construire un projet autour d’elle. Cela a commencé comme un projet de master, devenu ensuite un projet de doctorat de Lucija Mance, une excellente doctorante. Un grand merci à Franck, Sébastien, Martine, et à tous les autres formidables co-auteurs et collaborateurs d’Orléans, Rennes, Paris/Gif-sur-Yvette et Marseille. Et nous sommes aussi très heureux d’avoir pu coordonner une publication dos-à-dos avec les groupes de Paul Park, Jiho Park, Fischer et Ebert du Dana-Farber/Harvard. Leur article vient également d’être publié.
DELTEX E3 ligases ubiquitylate ADP-ribosyl modification on nucleic acids
Kang, Z. ✉, Suskiewicz, M.J., Chatrin, C., Strømland, Ø., Dorsey, B. W., Aucagne, V., Ahel, D. ✉, Ahel, I. ✉
Nucleic Acids Research, 24 November 2023, gkad1119
Lien vers l’article en libre accès
Ceci est la continuation d’une étude publiée l’année précédente et disponible ici. Les deux ont été menées principalement par Kang et Ivan, avec des contributions d’autres auteurs dont moi, en particulier sur l’article précédent. J’ai aussi été très content que cela devienne une collaboration avec un autre scientifique du CBM à Orléans, notre ami chimiste, Vincent Aucagne.
Pour ceux d’entre vous qui ne sont pas familiers avec l’ADP-ribosylation, je devrais peut-être commencer par dire que le NAD+ n’est pas seulement une molécule centrale du métabolisme énergétique dans la cellule, mais qu’il peut aussi être utilisé pour un type particulier de modification protéique appelé ADP-ribosylation, catalysé par la famille d’enzymes appelées PARPs. Lors de l’ADP-ribosylation, une petite partie du NAD+ appelée nicotinamide se détache et le reste du NAD+ (la partie ADP-ribose) se fixe de manière covalente à une protéine par le carbone auquel la nicotinamide était attachée.
Quelques PARPs semblent être des pseudo-enzymes en réalité inactives. L’une d’elles est PARP9, qui forme un complexe constitutif avec une ligase E3 d’ubiquitine, DTX3L. J’ai dit que PARP9 semble inactive, mais quand elle est en présence de DTX3L et de composants de la cascade d’ubiquitine (une enzyme E1, une enzyme E2, l’ATP), une réaction robuste entre le NAD+ et l’ubiquitine est observée, comme l’a démontré le groupe de Paschal il y a six ans.
En présence de ces composants (PARP9, DTX3L, E1, E2, et ATP), le NAD+ (ou une partie de celui-ci) se retrouve d’une façon ou d’une autre lié à l’ubiquitine. Quelle est donc cette réaction ? Il a été proposé qu’il s’agissait d’une ADP-ribosylation de l’ubiquitine : la nicotinamide se détacherait présumément du NAD+, la partie ADP-ribose du NAD+ se fixerait à l’ubiquitine par l’atome de carbone de l’ADP-ribose auquel la nicotinamide était attachée. Exactement comme dans tout autre événement d’ADP-ribosylation protéique catalysé par les PARPs.
Je dois mentionner que quelques années plus tard, le groupe de Huang – et en particulier Chatrin Chatrin, qui a depuis rejoint le groupe d’Ivan et est co-auteur de l’article NAR de Kang – a montré que, en fait, PARP9 est dispensable pour la réaction. Il faut une protéine DTX – soit DTX3L, soit l’un de ses homologues humains de la famille DTX – ainsi que E1, E2, et ATP. Le fragment minimal de DTX3L nécessaire est le domaine RING et un domaine adjacent de liaison au NAD+/ADP-ribose appelé DTC.
Qu’ont apporté les deux articles de Kang à cette histoire ? Ils ont montré – de manière convaincante, à mon avis – que cette mystérieuse réaction in vitro entre le NAD+ et l’ubiquitine que les protéines DTX catalysent n’est pas de l’ADP-ribosylation canonique. La nicotinamide ne se détache pas, le NAD+ reste intact, et l’ubiquitine se lie de manière covalente par une liaison ester à l’un des groupes hydroxyle du ribose du NAD+. Vincent Aucagne (avec l’aide de Hervé Meudal de notre plateforme RMN) a joué un rôle essentiel dans l’identification du site d’attachement de l’Ub.
On ne déplace pas la nicotinamide pendant la réaction et, en fait, la nicotinamide n’a même pas besoin d’être présente. Ainsi, la réaction DTX fonctionne également avec l’ADP-ribose. En fait, l’ADP-ribose est préféré au NAD+ comme substrat. Et – surtout – les enzymes DTX peuvent ubiquitylater l’ADP-ribose fixé à une protéine ou un peptide via une réaction d’ADP-ribosylation antérieure.
C’est une chimie nouvelle, et potentiellement très intéressante, car on ubiquityle une protéine non pas sur un résidu lysine, ce qui serait typique, mais sur une modification post-traductionnelle d’ADP-ribose. Et il en résulte une double modification ubiquitine-ADP-ribose qui pourrait peut-être avoir sa propre fonction distincte dans la cellule ?
Et maintenant un rebondissement supplémentaire. DTX3L s’avère posséder des domaines de liaison aux acides nucléiques. Il a été récemment montré que certaines PARPs peuvent ADP-ribosyler non seulement des protéines mais aussi des acides nucléiques (si cela se produit réellement dans la cellule n’est pas encore clair). DTX3L pourrait-elle donc ubiquitylater l’ADP-ribose fixé aux acides nucléiques ? Il s’avère que oui, et de manière plus robuste si une protéine entière avec des domaines de liaison aux acides nucléiques est utilisée.
Un point important : ces études décrivent des réactions in vitro assez robustes et spécifiques, mais elles restent à démontrer dans la cellule.
Et le dernier point. Je suis conscient qu’il y a une erreur dans la formule de l’ADP-ribose dans les schémas des deux articles : un ribose a une stéréochimie erronée. L’erreur vient de moi et est embarrassante étant donné que je travaille sur l’ADP-ribose depuis quelques années. Je suis reconnaissant à un chimiste présent lors d’un de mes séminaires l’été dernier qui m’a signalé quelque chose que j’avais toujours négligé. Je m’excuse auprès de Kang et des autres collègues qui, en me faisant confiance, ont copié ou ignoré cette erreur. J’espère que cela ne distraira pas le lecteur des élégantes expériences de Kang et de leurs conclusions fascinantes.
ADP-ribosylation from molecular mechanisms to therapeutic implications
Suskiewicz, M. J., Prokhorova, E., Rack, J.G.M., Ahel, I.✉
Cell, 2023, Oct 12;186(21):4475-95.
Lien vers l’article en libre accès
Une nouvelle revue complète sur l’ADP-ribosylation, rédigée avec d’anciens collègues du groupe d’Ivan Ahel à la Dunn School d’Oxford (je suis très reconnaissant à Ivan pour cette opportunité et à Evgeniia et Johannes pour le travail ensemble).
L’ADP-ribosylation est une réaction de modification biochimique fondamentale où l’ADP-ribose est transféré du NAD+ à un substrat (typiquement une protéine). Plusieurs cycles d’ADP-ribosylation peuvent aboutir à la formation de chaînes de poly(ADP-ribose). La modification par l’ADP-ribose peut réguler divers aspects de la fonction biomoléculaire, en particulier les interactions. Comme il existe plusieurs domaines et motifs protéiques qui reconnaissent l’ADP-ribosylation, la modification peut induire de nouvelles interactions protéine:protéine. Les inhibiteurs de la principale enzyme humaine d’ADP-ribosylation, PARP1, ont été utilisés avec succès en clinique pour cibler certains types de cancers. Dans cette revue, rédigée au cours de plusieurs mois, nous avons tenté de couvrir un large spectre, allant de la chimie à la biologie structurale, aux mécanismes enzymatiques, aux diverses voies cellulaires, et enfin aux applications cliniques.
Je suis satisfait de cette revue, à l’exception du signe de charge positive (plus) qui a été ajouté par accident à l’étape de production sur la nicotinamide détachée dans la première figure.
Structural insights into the regulation of the human E2∼SUMO conjugate through analysis of its stable mimetic
Goffinont, S., Coste, F., Prieu-Serandon, P., Mance, L., Gaudon, V., Garnier, N., Castaing, B., Suskiewicz, M. J. ✉
Journal of Biological Chemistry, 2023, 299(7)
Lien vers l’article en libre accès
Lors de l’ubiquitylation et des réactions apparentées, l’ubiquitine ou un modificateur apparenté est d’abord chargé sur un résidu Cys d’une enzyme E2, produisant un thioester E2-modificateur. Le modificateur est ensuite transféré de là sur un résidu Lys d’un substrat protéique, souvent avec l’aide d’une ligase E3.
La SUMOylation est une modification essentielle de type ubiquitine. Tandis que l’ubiquitylation repose sur de nombreuses E2, la SUMOylation dépend d’une seule, UBC9, qui est donc la protéine centrale de la voie. UBC9 est hautement conservée, sa séquence variant peu de la levure à l’humain.
Les thioesters E2-modificateur étant instables, notre objectif ici était de produire un mimétique stable du complexe UBC9-SUMO humain. Nous avons utilisé une stratégie développée par l’excellent groupe de Lima pour l’Ubc9 de levure, qui consiste à introduire un résidu Lys à proximité spatiale de la Cys93 du site actif d’UBC9. Nous décrivons notre mise en œuvre de cette stratégie en détail, et montrons que SUMO migre efficacement de la Cys93 vers une Lys placée en position 129 par la mutation Ala129Lys, formant une molécule stable avec SUMO fixé à 3 Å de sa position native dans le thioester UBC9-SUMO.
Nous avons cristallisé ce mimétique. En l’absence d’une ligase E3, il adopte la conformation dite ouverte, qui correspondrait vraisemblablement à un état inactif du thioester. En effet, toutes les structures précédentes d’UBC9-SUMO étaient en présence d’une ligase E3, qui stabilisait l’état fermé. De manière intéressante, dans le cristal, le mimétique forme des chaînes via une interaction non-covalente entre SUMO d’une molécule d’UBC9-SUMO et UBC9 de la suivante. Nous pensons que de telles interactions peuvent parfois se former dans les cellules, décourageant stériquement l’état actif, fermé, d’UBC9-SUMO. Un autre point intéressant concerne la Cys138, une Cys exposée en surface d’UBC9 avec une fonction peu claire. Dans notre structure cristalline en conformation ouverte, la Cys138 est proche de la Cys52 de SUMO et elles se sont apparemment pontées par le DTT. Ces résidus Cys pourraient-ils former un pont disulfure dans certaines conditions cellulaires ?
Il y a d’autres éléments dans cette histoire aussi. Nous avons mis l’accent sur une description et une discussion détaillées. Nous serions heureux si cela est utile au domaine.
Cela fait partie d’une ligne de recherche plus large où nous essayons différentes approches biochimiques et chimiques pour stabiliser les complexes de SUMOylation. C’est la première publication de notre projet SUMOwriteNread. Notre ingénieur Stéphane Goffinont a joué le premier rôle (merci et félicitations !), avec l’aide de Franck Coste (structure cristalline), Pierre Prieu-Serandon, et le reste de l’équipe.
Nous avons une courte description vulgarisée de l’article en anglais sur le site de notre Centre.
Updated protein domain annotation of the PARP protein family sheds new light on biological function
Suskiewicz, M. J. ✉✱, Munnur, D.✱, Strømland, Ø.✱, Yang, J. C., Easton, L. E., Chatrin, C., Zhu, K., Baretić, D., Goffinont, S., Schuller, M., Wu, W.-F., Elkins, J. M., Ahel, A., Sanyal, S., Neuhaus, D., Ahel, I. ✉
Nucleic Acids Research, 2023, 51(15):8217-8236
Lien vers l’article en libre accès
Dans cet article issu d’un projet annexe, nous avons soigneusement analysé les modèles AlphaFold2 des membres humains de la famille de protéines PARP, réalisé une annotation complète des domaines, apporté de nouvelles perspectives sur la structure et la fonction, et validé expérimentalement certaines d’entre elles.
Nous espérons que l’annotation des domaines sera une ressource utile. Nous pensons que tous les domaines structurés au sein des PARPs sont maintenant identifiés. Certains n’avaient pas été rapportés auparavant – par exemple, les domaines KH, qui sont des domaines potentiels de liaison à l’ARN ou à l’ADN simple brin avec spécificité de séquence, au sein de PARP9, 10 et 14.
J’ai réalisé la majeure partie de l’analyse computationnelle et de la rédaction, tandis que Deeksha et Øyvind du laboratoire d’Ivan Ahel (mon ancien groupe) ont effectué des expériences démontrant que des fragments de PARP14 peuvent effectivement se lier aux acides nucléiques et les ADP-ribosyler in vitro. L’équipe de David Neuhaus au MRC LMB de Cambridge a contribué une intéressante expérience de RMN montrant que, tandis que les domaines individuels de PARP1 ont une mobilité indépendante en l’absence d’ADN, la plupart d’entre eux se regroupent lors de la liaison à une cassure d’ADN – à l’exception du domaine BRCT, qui reste flexible.
Dans l’introduction, nous avons essayé d’expliquer de manière simple les principes sous-jacents d’AlphaFold2 et de présenter divers outils récents et faciles à utiliser pour l’analyse des protéines. Nous espérons que cette partie pourrait intéresser même les personnes travaillant sur d’autres familles de protéines.
L’Institut de Chimie du CNRS a consacré à cet article un bel article de vulgarisation en français, et nous avons une courte note en anglais sur le site de notre Centre également.